最近在做质谱数据分析,不得不说,从原始数据开始分析东西实在是太恶心了。数据预处理要逼疯我……
对MALDI-MSI 的每个section聚类,可以用Spatial Shrunken Centroids 的方法。这个方法来自文章Probabilistic Segmentation of Mass Spectrometry (MS) Images Helps Select Important Ions and Characterize Confidence in the Resulting Segments,代码可以在Cardinal 这个R package里找到。
我主要用聚类,所以就只总结聚类,分类应该差不多。
这个方法是两个算法的结合:
Shrunken Centroids 和 Spatially Aware (SA) and Spatially Aware Structurally Adaptive (SASA) Distances
本身 Spatially Aware (SA)这篇文章就也是一个image segmentation 的文章,它用SA定义了距离之后,再用kmeans做的聚类。
但本文,可以说是基于SA这篇文章做的改进,算法的大体思路是:
1)用SA那篇文章将一个section分成K个类;
2)计算整个section的质心 X ˉ \bar{X} Xˉ
3) 对于每一个segmentation,计算聚类内部的质心 X ˉ k \bar{X}_k Xˉk
4) 对于每个feature, 计算每一个类的质心到section质心的t统计量

讯享网
5)定义一个Shrunken parameter s,让SA生成的质心们向总质心靠拢
具体方法是:通过公式2 ,更新每个特征的统计量。让统计量低的特征的统计量清零,统计量高的减去s。再用公式3更新每一个类的质心。简而言之就是收缩整个类相对于整体质心的统计量,使质心向整体的质心靠拢。
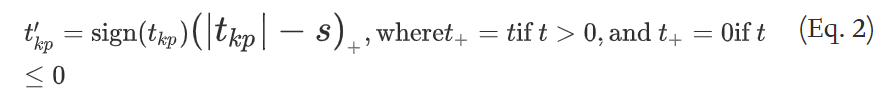
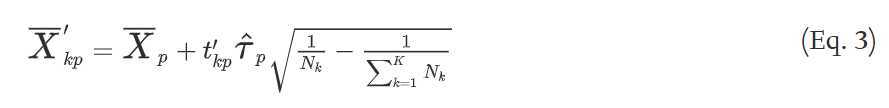

6)这样就得到了k个新的质心 X ˉ k ′ {\bar{X}}'_k Xˉk′
7) 对于每个像素,计算它们到各个质心的SA距离;(公式8,后面细说)
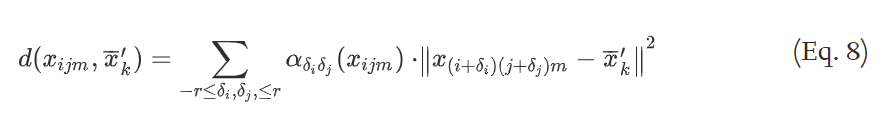
8) 通过公式10调整公式8的距离,聚类中, π k = 1 / K π_k = 1/K πk=1/K
然后通过公式11,将像素分配给概率最高的类。
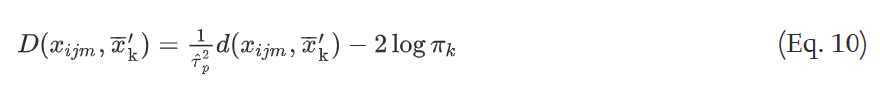

9)在得到了最新的分割结果后,返回步骤3),重新执行分割步骤3)~8),如此循环直至分割结果不再改变,或者达到最大迭代次数。
方法不难理解,其中一个关键点是SA的计算方法。和普通计算两点之间的距离不同,质谱数据是数据立方体,不仅有数以千计的m/z作为特征,像素和像素之间也不是独立的。因此SA综合考虑了像素以及其近邻的intensity,计算 其与另外一个pixel以及其近邻的“综合距离”。这是一篇2013年bioinformatics上的文章 Efficient spatial segmentation of large imaging mass spectrometry datasets with spatially aware clustering。
这个方法明天再补吧。。
Reference
- Alexandrov, T., & Kobarg, J. H. (2011). Efficient spatial segmentation of large imaging mass spectrometry datasets with spatially aware clustering. Bioinformatics, 27(13), i230-i238. doi:10.1093/bioinformatics/btr246
- Tibshirani, R., Hastie, T., Narasimhan, B., & Chu, G. (2003). Class Prediction by Nearest Shrunken Centroids, with Applications to DNA Microarrays. Statistical Science, 18, 104-117.
- Bemis, K.D., Harry, A., Eberlin,L.S., Ferreira, C.R., van de Ven, S.M., Mallick, P., Stolowitz, M.and Vitek, O., 2016. Probabilistic segmentation of mass spectrometry(MS) images helps select important ions and characterize confidence in the resulting segments. Molecular & Cellular Proteomics, 15(5), pp.1761-1772.

版权声明:本文内容由互联网用户自发贡献,该文观点仅代表作者本人。本站仅提供信息存储空间服务,不拥有所有权,不承担相关法律责任。如发现本站有涉嫌侵权/违法违规的内容,请联系我们,一经查实,本站将立刻删除。
如需转载请保留出处:https://51itzy.com/kjqy/12743.html