KOBAS(KEGG Orthology Based Annotation System),,是由北京大学魏文丽课题组开发的数据库,主要功能是用于基因/蛋白质功能注释和功能富集。随着数据量不断增加,KOBAS至今为止共经历了3次升级,除了1.0版本的KEGG代谢通路之外,2.0版本增加了PID Curated,PID BioCarta,PID Reactome,BioCyc,Reactome和Panther等数据库,除此之外还增加了疾病的查询,使得KOBAS的功能更加强大。而3.0版本更是增加了lncRNA的鉴定、注释以及富集功能,还建立GSEA,GSA和 PADOG等功能。
KOBAS的功能最主要分为两个部分,Annotate(注释)和Enrichment(富集)。
接下来我们就以“Annotate”为例来体验看看如何利用KOBAS做GO和KEGG的富集分析吧!
点击“Annotate”选项,进入注释界面。
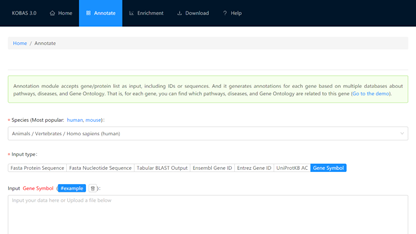

“Species”为物种,可根据自己测序组织来源进行选择,如人,大鼠,小鼠等。
“Input Type”为输入格式/类型,支持如图Fasta Protein Sequence,Gene Symbol等七种格式,可根据自己的输入数据进行选择。
文章剩余内容<<<<<<

版权声明:本文内容由互联网用户自发贡献,该文观点仅代表作者本人。本站仅提供信息存储空间服务,不拥有所有权,不承担相关法律责任。如发现本站有涉嫌侵权/违法违规的内容,请联系我们,一经查实,本站将立刻删除。
如需转载请保留出处:https://51itzy.com/kjqy/126349.html