遗传算法
一、介绍
遗传算法是用于解决最优化问题的一种搜索算法。遗传算法借用了生物学里达尔文的进化理论:“适者生存,优胜劣汰”,将该理论以算法的形式表现出来就是遗传算法的过程。
二、基本原理
1)程序流程
遗传算法是通过大量备选解的变换、迭代和变异,在解空间中并行动态地进行全局搜索的最优化方法,是模拟生物基因遗传的做法,算法的基本原理通过编码组成的群体组成初始群体后,遗传操作的任务就算对群体的个体按照他们对环境适应度(适应度)评估,施加了一定的操作之后从而实现优胜劣汰的进化过程,算法的基本程序框图:
2)物竞天择
我们可以假设有一个种群,这个种群存在的目标是帮我寻找一个函数F(x)的极值(可能是max or min),首先我们随机生成一组种群,假设我对变量x的取值范围为【0,8】,这是我们的变量域,因为我们要玩一些不一样的操作,先跟着我,后面你会恍然大悟!我们会有一个二进制域【0,2^8】,我们的二进制域对应的就是我们的变量域,我们将数字8看成8位的二进制数,可以得到2的八次方为:256,但因为我们在二进制当中我们是从0开始的,0-255,有256个数,我们的八位二进制数最多只能取到255,取不到256。
"二进制" 0 0 0 0 0 0 0 0 "二进制数 x-> " 1 1 1 1 1 1 1 1 "x转化为十进制" 1*2^0 + 1*2^1 + 1*2^2 + 1*2^3 + 1*2^4 + 1*2^5 + 1*2^6 + 1*2^7 = 255 讯享网
因为我们实数x的范围只有【0,8】,我们将二进制转化为十进制之后,还有求解二进制域到变量域值,二进制域到变量域之间的映射关系为:
讯享网"变量域x_" x_ = x*8/2^8
如此,我们将我们的8看作是染色体的长度,这样我们就可以做一些基因重组和基因变异的操作了!!!,我们先来一组基因重组图:
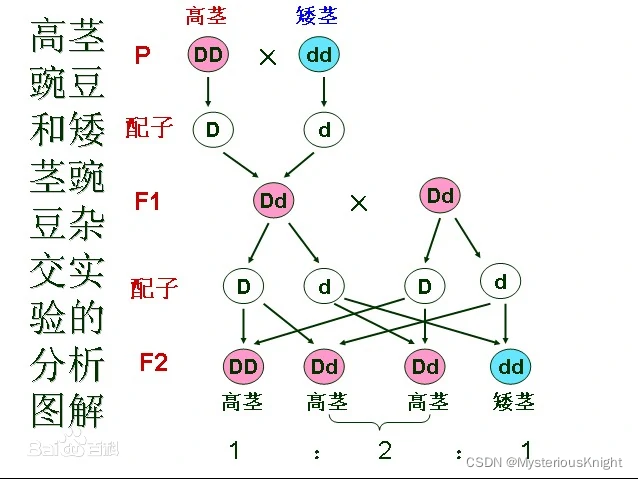
是不是很熟悉,这个不就是高中生物的杂交实验吗?如果我们把DD和dd看成我们染色体的0和1呢?我们再形象一点
# 定义我们的染色体 x1 = [0 1 0 0 1 0 0 1] x2 = [1 1 0 1 0 0 0 1] #OK 我们现在有两个种群了(抽象一点) # 第一个种群 x1 的染色体为 0 1 0 0 1 0 0 1 # 第一个种群 x2 的染色体为 1 1 0 1 0 0 0 1 #我们尝试做一下杂交实验?学一学孟德尔的八年抗战 "第一代:" 0 1 0 0 1 0 0 1 * 1 1 0 1 0 0 0 1 | | v v "配子:" [0 1 0 0] [1 0 0 1 ] [1 1 0 1 ] [0 0 0 1] #用x1的第一个配子和x2的第二个配子进行基因重组 #用x1的第二个配子和x2的第一个配子进行基因重组 "F1代:" [0 1 0 0][0 0 0 1] [1 1 0 1 ][1 0 0 1] new_x1 = [0 1 0 0 0 0 0 1] new_x2 = [1 1 0 1 1 0 0 1] # 不知道你有没有恍然大悟 有了二进制的操作,我们做变异的时候也是同样的道理,我们只需要把0变异为1,1变异为0,就能完成我们的变异算法。
3)算法步骤
求解函数:f(x) = 9sin(5x) + 7cos(4*x)的最大值,x的取值范围为【0,8】
3.1初始化种群
我们先初始化我们的种群,先初始化一些随机解,因为我们要在搜索空间内寻找我们的最优解,可参考粒子群算法的思想。
讯享网def initpop(popsize, chromlength): """ Parameters ---------- popsize : TYPE 种群的数目. chromlength : TYPE 表示染色体的长度(二值数的长度), 长度的大小取决于变量的二进制编码的长度 Returns ------- pop : TYPE 随机种群 """ pop=np.round(np.random.rand(popsize,chromlength)) return pop
3.2二进制编码转化为十进制数
设计我们的算法,将二进制的矩阵转化为十进制数,为了得到我们的二进制域。
def decodebinary(pop): """ 二进制数转十进制数函数 Parameters ---------- pop : TYPE 初始化种群. Returns ------- pop2 种群的染色体二进制数转十进制数 """ px,py = pop.shape pop1 = np.zeros((px,py)) for i in range(py): pop1[:,i] = (2(py-i-1))*pop[:,i] pop2=np.sum(pop1, 1)#对pop1向量的每行求和 标识位0代表每列求和,标识位1代表每行求和 return pop2 def encode(bestpop): """ 解码x的值 Parameters ---------- bestpop : TYPE 最好的个体. Returns ------- x : TYPE 最优X的取值. """ temp = decodebinary(pop) x=temp*15/32767 return x 我们的pop2是一个转化为十进制数之后的种群,可以理解为种群的表现型,我们的0和1的操作反应的是种群的基因型,因为我们的变量不可能只有一种,扩展我们的思维,我们先设置的染色体长度,因为我们的变量只有一个,它的值域在【0,8】,如果我们有两个变量,不同变量对应不同值域,我们的染色体的长度是否也要切片计算?仔细思考。
讯享网def decodechrom(pop,spoint,length): """ 将二进制编码转化为十进制数 Parameters ---------- pop : TYPE DESCRIPTION. spoint : TYPE 染色体的起始位. length : TYPE DESCRIPTION. Returns ------- pop2 : TYPE DESCRIPTION. """ #对于多个变量而言,如有两个变量,采用20为表示,每个变量10位,则第一个变量从1开始,另一个变量从11开始。本例为一个变量 #这句话的意思就是加入目标函数需要两个变量,则我可将染色体的数量拆为两个,然后遗传迭代 #值得注意的是,我的染色体的长度也要跟着变量的数量改变,呈倍数关系 pop1=pop[:,spoint:spoint+length] pop2=decodebinary(pop1) return pop2
这里的spoint代表的是我们的一个终止位,可以对我们的变量进行一个切片,自行理解。

3.3实现目标函数的计算
实现目标函数的计算,就是把x的值带进去,很简单。
def calobjvalue(pop): """ 实现目标函数的计算 Parameters ---------- pop : TYPE 种群. Returns ------- objvalue : TYPE 返回目标函数值. """ temp = decodechrom(pop, 0, 15) x=temp*15/32767 objvalue = 9*np.sin(5*x)+7*np.cos(4*x) objvalue = np.reshape(objvalue,(-1,1))#以行的形式输出 return objvalue 3.4剔除0以外的值
计算个体的适应值,在calobjvalue已经计算好,需要将小于0的个体删除,方便后续的概率计算。
讯享网def calfitvalue(objvalue): """ 计算个体的适应值,在calobjvalue已经计算好,需要将小于0的个体删除,方便后续的概率计算 Parameters ---------- objvalue : TYPE 目标函数值. Returns ------- fitvalue : TYPE 个体适应值. """ global Cmin Cmin = 0 fitvalue = np.zeros((objvalue.shape[0],objvalue.shape[1])) px, py = objvalue.shape for i in range(px): if objvalue[i,0] + Cmin > 0: temp = objvalue[i,0] + Cmin else: temp = 0 fitvalue[i,0]=temp return fitvalue
3.5选择算法
选择算法我们采用轮盘赌,决定哪些个体可以进入下一代,用轮盘赌选择复制
def selection(pop, fitvalue): """ 选择函数 选择复制,决定哪些个体可以进入下一代 采用轮盘赌选择 Parameters ---------- pop : TYPE 种群的个体. fitvalue : TYPE 个体适应值. Returns ------- newpop : dict 新的种群. """ totalfit = np.sum(fitvalue) fitvalue_pro = fitvalue / (totalfit + 0.000001) fitvalue_pro_cumnsum = np.cumsum(fitvalue_pro) fitvalue_pro_cumnsum = np.reshape(fitvalue_pro_cumnsum,(-1,1))#以行的形式 px, py = pop.shape #轮盘随机概率 从小到大排序 ms = np.sort(np.random.rand(px,1),0) fitin = 1 - 1 #pop种群 第几代个体 因为python的下标从0开始。所以是第一代的索引是0 故用1-1 newin = 1 - 1 #pop种群 第几代个体 newpop_dict = {
} #我愿称为[适者生存,优胜劣汰] while循环 while newin <= px-1: if ms[newin, 0] < fitvalue_pro_cumnsum[fitin, 0]: newpop_dict[newin] = pop[fitin,:] newin += 1 else: fitin += 1 newpop = np.zeros((newin,py)) for i in range(newin): newpop[i,:] = newpop_dict[i] return newpop 3.6交叉算法(基因重组)
物竞天择是遗传学的核心,相应的,选择和变异也是遗传算法的核心,我们对染色体进行一个基因重组的操作,具体代码如下:
讯享网def crossover(pop, pc): """ 交叉算法 实现基因重组 Parameters ---------- pop : TYPE 种群. pc : TYPE 交叉概率. Returns ------- newpop : TYPE DESCRIPTION. """ px, py = pop.shape newpop = np.zeros((px, py)) # seletion_litst = [i for i in range(px)] # sl = seletion_litst[0:px:2] for i in range(px-1): #是否能够进行基因重组 if pc > np.random.rand(1)[0]: cpoint = int(np.round(np.random.rand(1)[0] * py) - 1) if cpoint == 0: cpoint = 1 newpop[i, :][0:cpoint] = pop[i, 0:cpoint] newpop[i, :][cpoint+1:py] = pop[i+1, cpoint+1:py] newpop[i+1, :][0:cpoint] = pop[i+1, 0:cpoint] newpop[i+1, :][cpoint+1:py] = pop[i, cpoint+1:py] else: newpop[i,:] = pop[i,:] newpop[i+1,:] = pop[i+1,:] return newpop
3.7变异算法(基因突变)
0变1,1变0 你上你也行
def mutation(pop, pm): """ 变异算法 实现基因突变 Parameters ---------- pop : TYPE 种群. pm : TYPE 变异概率. Returns ------- newpop : TYPE 新的变异种群. """ px, py = pop.shape newpop = np.zeros((px, py)) for i in range(px): if pm > np.random.rand(1)[0]: mpoint = int(np.round(np.random.rand(1)[0] * py) - 1) if mpoint == 0: mpoint = 1 newpop[i,:] = pop[i,:] if newpop[i, mpoint] == 0: newpop[i, mpoint] = 1 newpop[i,:] = pop[i,:] return newpop 3.7最优计算(基因突变)
简单的排序取最大(不要忘记我们粒子群算法里面的全局极值和个体极值)
讯享网def best(pop, fitvalue): """ 最优的个体及其适应值 Parameters ---------- pop : TYPE 种群. fitvalue : TYPE 适应值. Returns ------- bestindividual : 最大适应值 DESCRIPTION. bestfit : TYPE 最大适应值的个体. """ px, py = pop.shape bestindividual = pop[0,:] bestfit = fitvalue[0] for i in range(1,px): if fitvalue[i] > bestfit: bestindividual = pop[i,:] bestfit = fitvalue[i] return bestindividual,bestfit
3.完整代码
不要忘记导入我们的numpy 和matplotlib库,将上面的函数和导入的库,放在主函数的上面,然后运行代码,不过我这里的取值是【0,15】,上面说【0,8】便于读者理解。
import numpy as np import matplotlib.pyplot as plt # 遗传算法 def initpop(popsize, chromlength): """ Parameters ---------- popsize : TYPE 种群的数目. chromlength : TYPE 表示染色体的长度(二值数的长度), 长度的大小取决于变量的二进制编码的长度 Returns ------- pop : TYPE 随机种群 """ pop=np.round(np.random.rand(popsize,chromlength)) return pop def decodebinary(pop): """ 二进制数转十进制数函数 Parameters ---------- pop : TYPE 初始化种群. Returns ------- pop2 种群的染色体二进制数转十进制数 """ px,py = pop.shape pop1 = np.zeros((px,py)) for i in range(py): pop1[:,i] = (2(py-i-1))*pop[:,i] pop2=np.sum(pop1, 1)#对pop1向量的每行求和 标识位0代表每列求和,标识位1代表每行求和 return pop2 def decodechrom(pop,spoint,length): """ 将二进制编码转化为十进制数 Parameters ---------- pop : TYPE DESCRIPTION. spoint : TYPE 染色体的起始位. length : TYPE DESCRIPTION. Returns ------- pop2 : TYPE DESCRIPTION. """ #对于多个变量而言,如有两个变量,采用20为表示,每个变量10位,则第一个变量从1开始,另一个变量从11开始。本例为一个变量 #这句话的意思就是加入目标函数需要两个变量,则我可将染色体的数量拆为两个,然后遗传迭代 #值得注意的是,我的染色体的长度也要跟着变量的数量改变,呈倍数关系 pop1=pop[:,spoint:spoint+length] pop2=decodebinary(pop1) return pop2 def encode(bestpop): """ 解码x的值 Parameters ---------- bestpop : TYPE 最好的个体. Returns ------- x : TYPE 最优X的取值. """ temp = decodebinary(pop) x=temp*15/32767 return x def calobjvalue(pop): """ 实现目标函数的计算 Parameters ---------- pop : TYPE 种群. Returns ------- objvalue : TYPE 返回目标函数值. """ temp = decodechrom(pop, 0, 15) x=temp*15/32767 objvalue = 9*np.sin(5*x)+7*np.cos(4*x) objvalue = np.reshape(objvalue,(-1,1))#以行的形式输出 return objvalue def calfitvalue(objvalue): """ 计算个体的适应值,在calobjvalue已经计算好,需要将小于0的个体删除,方便后续的概率计算 Parameters ---------- objvalue : TYPE 目标函数值. Returns ------- fitvalue : TYPE 个体适应值. """ global Cmin Cmin = 0 fitvalue = np.zeros((objvalue.shape[0],objvalue.shape[1])) px, py = objvalue.shape for i in range(px): if objvalue[i,0] + Cmin > 0: temp = objvalue[i,0] + Cmin else: temp = 0 fitvalue[i,0]=temp return fitvalue def selection(pop, fitvalue): """ 选择函数 选择复制,决定哪些个体可以进入下一代 采用轮盘赌选择 Parameters ---------- pop : TYPE 种群的个体. fitvalue : TYPE 个体适应值. Returns ------- newpop : dict 新的种群. """ totalfit = np.sum(fitvalue) fitvalue_pro = fitvalue / (totalfit + 0.000001) fitvalue_pro_cumnsum = np.cumsum(fitvalue_pro) fitvalue_pro_cumnsum = np.reshape(fitvalue_pro_cumnsum,(-1,1))#以行的形式 px, py = pop.shape #轮盘随机概率 从小到大排序 ms = np.sort(np.random.rand(px,1),0) fitin = 1 - 1 #pop种群 第几代个体 因为python的下标从0开始。所以是第一代的索引是0 故用1-1 newin = 1 - 1 #pop种群 第几代个体 newpop_dict = {
} #我愿称为[适者生存,优胜劣汰] while循环 while newin <= px-1: if ms[newin, 0] < fitvalue_pro_cumnsum[fitin, 0]: newpop_dict[newin] = pop[fitin,:] newin += 1 else: fitin += 1 newpop = np.zeros((newin,py)) for i in range(newin): newpop[i,:] = newpop_dict[i] return newpop def crossover(pop, pc): """ 交叉算法 实现基因重组 Parameters ---------- pop : TYPE 种群. pc : TYPE 交叉概率. Returns ------- newpop : TYPE DESCRIPTION. """ px, py = pop.shape newpop = np.zeros((px, py)) # seletion_litst = [i for i in range(px)] # sl = seletion_litst[0:px:2] for i in range(px-1): #是否能够进行基因重组 if pc > np.random.rand(1)[0]: cpoint = int(np.round(np.random.rand(1)[0] * py) - 1) if cpoint == 0: cpoint = 1 newpop[i, :][0:cpoint] = pop[i, 0:cpoint] newpop[i, :][cpoint+1:py] = pop[i+1, cpoint+1:py] newpop[i+1, :][0:cpoint] = pop[i+1, 0:cpoint] newpop[i+1, :][cpoint+1:py] = pop[i, cpoint+1:py] else: newpop[i,:] = pop[i,:] newpop[i+1,:] = pop[i+1,:] return newpop def mutation(pop, pm): """ 变异算法 实现基因突变 Parameters ---------- pop : TYPE 种群. pm : TYPE 变异概率. Returns ------- newpop : TYPE 新的变异种群. """ px, py = pop.shape newpop = np.zeros((px, py)) for i in range(px): if pm > np.random.rand(1)[0]: mpoint = int(np.round(np.random.rand(1)[0] * py) - 1) if mpoint == 0: mpoint = 1 newpop[i,:] = pop[i,:] if newpop[i, mpoint] == 0: newpop[i, mpoint] = 1 newpop[i,:] = pop[i,:] return newpop def best(pop, fitvalue): """ 最优的个体及其适应值 Parameters ---------- pop : TYPE 种群. fitvalue : TYPE 适应值. Returns ------- bestindividual : 最大适应值 DESCRIPTION. bestfit : TYPE 最大适应值的个体. """ px, py = pop.shape bestindividual = pop[0,:] bestfit = fitvalue[0] for i in range(1,px): if fitvalue[i] > bestfit: bestindividual = pop[i,:] bestfit = fitvalue[i] return bestindividual,bestfit if __name__ == "__main__": popsize=30; #群体大小 chromlength=15; #字符串长度(染色体的长度) pc=0.7; #交叉概率 pm=0.005 #变异概率 #初始化种群 pop=initpop(popsize, chromlength) poptest=pop #开始迭代 epoch = 200 x_ = [] y_ = [] for i in range(epoch): objvalue = calobjvalue(pop) #计算目标函数值 fitvalue = calfitvalue(objvalue) #计算群体中每个个体的适应度 newpop = selection(pop, fitvalue) newpop1 = crossover(newpop, pc) newpop2 = mutation(newpop1, pm) objvalue = calobjvalue(newpop2) #计算目标函数值 fitvalue = calfitvalue(objvalue) #计算群体中每个个体的适应度 bestindividual,bestfit = best(newpop2, fitvalue) #求出群体中适应值最大的个体及其适应值 x_.append(bestfit) pop = newpop2 plt.plot(x_, lw=3, label='funcotio_max_value_x') plt.show() reshape_best_infrivedual = np.reshape(bestindividual,(1,-1))#以行的形式 best_x_value = encode(reshape_best_infrivedual) plt.plot(x_, lw=3, label='funcotio_max_value_x') plt.legend() plt.show() print("最好的个体是 ",bestindividual) print("函数:f(x) = 9sin(5x)+7cos(4x)的极值为 ",bestfit[0]) #最后拟合之后随便取一个值即可 print("x的取值应为: ",best_x_value[0]) #最后拟合之后随便取一个值即可 4)运行结果
![[外链图片转存失败,源站可能有防盗链机制,建议将图片保存下来直接上传(img-gbMtHJ8N-1650549372734)(genetic.assets/image-20220421215451632.png)]](https://img-blog.csdnimg.cn/83d0ce505f2d4ebfa3fbd3d0b36e2ed0.png?x-oss-process=image/watermark,type_d3F5LXplbmhlaQ,shadow_50,text_Q1NETiBATXlzdGVyaW91c0tuaWdodA==,size_8,color_FFFFFF,t_70,g_se,x_16)
最好的个体是 [1. 0. 0. 0. 0. 1. 1. 0. 0. 0. 0. 0. 0. 0. 0.]
函数:f(x) = 9sin(5x)+7cos(4x)的极值为 15.6948
x的取值应为: 7.4557

版权声明:本文内容由互联网用户自发贡献,该文观点仅代表作者本人。本站仅提供信息存储空间服务,不拥有所有权,不承担相关法律责任。如发现本站有涉嫌侵权/违法违规的内容,请联系我们,一经查实,本站将立刻删除。
如需转载请保留出处:https://51itzy.com/kjqy/23694.html